
配列情報マルチ解析ソフトウェアGeneious

概要
Geneiousは、さまざまなバイオインフォマティクスツールを統合したマルチシーケンスデータ解析ソフトウェアです。
コマンドラインは一切不要で、誰にでもわかりやすく簡単に、数多くの解析ツールをご使用いただけます。
ツール間のファイルの移動や変換も不要なため、アラインメント、アセンブリ、マッピング、系統樹作成、アノテーション、BLAST検索、変異検出、発現解析などの解析を一括して行うことができます。
特徴
ワークフローによる自動解析
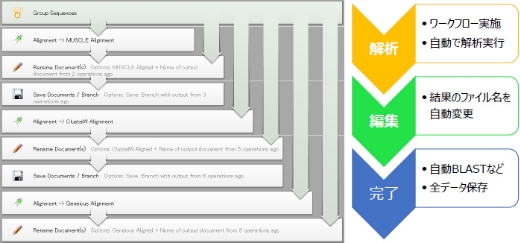
どなたが操作しても同じデータ解析フローを再現し、安定した結果を導き出す事が可能となります。
自動化ワークフローはコマンドライン不要!自身で作成可能で、解析設定も自由に編集できます。
アラインメント
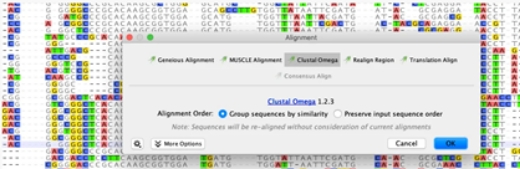
Clustal Omega, MUSCLE, MAFFTなど幅広いアルゴリズムを搭載しています。ヌクレオチド、アミノ酸どちらもアラインメントが可能で、アノテーションの付加や統計情報の表示、シークエンスの編集、変異/SNPs検出などが可能です。
アセンブリ/マッピング変異、SNPs検出/発現量解析
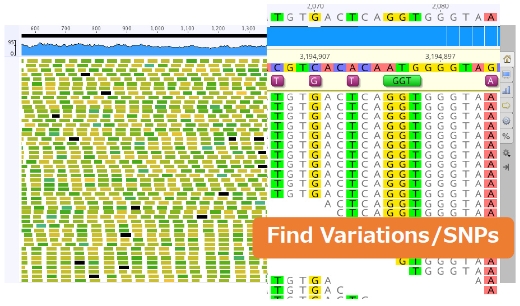
Geneious独自、Tadpole、Velvetなどのアセンブラ、ロングリード対応のMinimap2マッパーなどを搭載し、さまざまなリードデータをアセンブル、マッピングすることが可能です。リードのトリムも簡単に設定できます。
リファレンスシークエンスにマッピング後は、変異、 SNPs検出や発現量解析~CSV一覧までを容易に実行することが可能です。
Minimap2によるショート/ロングリード
シークエンスマッピング
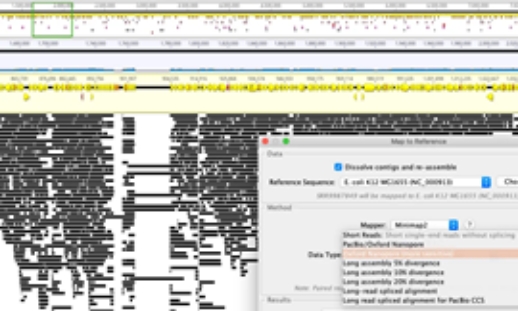
Minimap2は、Oxford NanoporeとPacBioのロングリードシークエンスをマッピングするのに適した汎用性の高いアライナーです。
コマンドライン不要で、最大15%のエラーを含むリードデータをリファレンスシークエンスにすばやく簡単にアラインメントすることができます。
系統樹作成
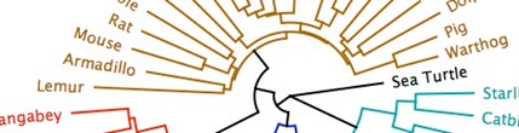
シークエンスリストやアラインメントから、簡単に系統樹の作成が可能です。NJ、UPGMA、MrBayes、PhyML、GARLI、RAxML、FastTreeなど、さまざまなアルゴリズムを搭載しています。ノード同士の距離によるヒートマップ化やCSVの出力も可能です
プライマーデザイン
クローニング/CRISPRサイト検索
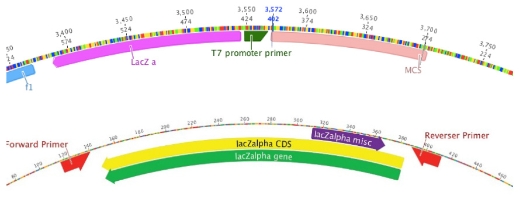
複数領域のプライマーの同時作成、作成したプライマーの編集、プロダクトのシミュレートも簡単に実行可能です。 二次構造、融点、GC含量も自動で計算されます。 クローニングのシミュレートや、PlasMapperによるターミネーター、制限酵素サイト、レポーター遺伝子、アフィニティタグなどのアノテーションも可能です。コドン最適化機能も搭載しています。
BLAST検索
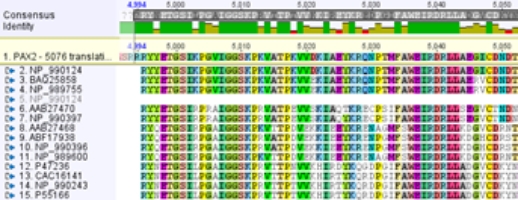
Genbankや、ご自分で作成したカスタムデータベースに対してBLAST検索し、目的配列との相同性検索を行うことができます。
ヒットした配列をアノテーション付きでダウンロードすることや、BLAST結果からアラインメントすることも可能です。
データ選択範囲の⾃動数値計算
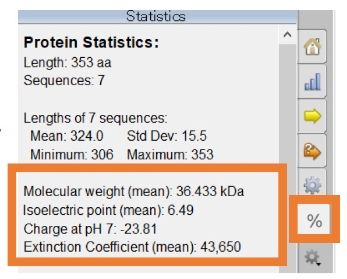
インポートしたデータの核酸配列・アミノ酸配列を選択するだけで、選択範囲の数値データが⾃動的に計算&表⽰されます。数値はコピー&ペーストが可能です。
⾃動計算データ例:
Length (bp), Rough Tm (°C), Molecular weight (kDa), GC content (%), Nucleotide/AA/Codon frequency (%), Isoelectric point, Charge at pH 7,
Extinction Coefficient
無料プラグインによる機能の拡張
Geneiousの解析を拡張するさまざまなプラグインが無料で提供されます。詳細は下記ページをご参照下さい。
https://www.geneious.com/plugins/
対応データ
幅広いデータベース由来のファイルをドラッグ&ドロップでインポート可能です。 また、Geneiousにインポートしたファイル、NCBIからダウンロードしたデータ、解析したデータを、FASTA/FASTQ, GFF, Genbank flat, VCFなど、さまざまな形式で出⼒することも可能です。
| Format | Extensions | Data types | Common sources |
|---|---|---|---|
| BED | *.bed | Annotations | UCSC |
| Common Assembly Format | *.caf | Contigs | Sequencher |
| Clustal | *.aln | Alignments | ClustalX |
| CSFASTA | *.csfasta | Color space FASTA | ABI SOLiD |
| DNAStar | *.seq, *.pro | Nucleotide & protein sequences | DNAStar |
| DNA Strider | *.str | Sequences | DNA Strider (Mac program), ApE |
| Embl/UniProt | *.embl, *.swp | Sequences | Embl, UniProt |
| Endnote (8.0 or 9.0) XML | *.xml | Journal article references | Endnote, Journal article websites |
| FASTA | *.fasta, *.fas, etc. | Sequences, alignments | PAUP*, ClustalX, BLAST, FASTA |
| FASTQ | *.fastq, *.fasq | Sequences with quality | Solexa/Illumina |
| GCG | *.seq | Sequences | GCG |
| GenBank | *.gb, *.xml | Nucleotide & protein sequences | GenBank |
| Geneious | *.xml, *.geneious | Preferences, databases | Geneious |
| Geneious Education | *.tutorial.zip | Tutorial, assignment etc. | Geneious |
| GFF | *.gff | Annotations | Sanger Artemis |
| MEGA | *.meg | Alignments | MEGA |
| Molecular structure | *.pdb, *.mol, *.xyz, *.cml, *.gpr, *.hin, *.nwo |
3D molecular structures | 3D structure databases and programs |
| Newick | *.tre, *.tree, etc. | Phylogenetic trees | PHYLIP, Tree-Puzzle, PAUP*, ClustalX |
| Nexus | *.nxs, *.nex | Trees, Alignments | PAUP*, Mesquite, MrBayes & MacClade |
| PDB | *.pdb | 3D Protein structures | SP3, SP2, SPARKS, Protein Data Bank |
| Documents, presentations | Adobe Writer, LATEX, Miktex | ||
| Phrap ACE | *.ace | Contig assemblies | Phrap/Consed |
| PileUp | *.msf | Alignments | pileup (gcg) |
| PIR/NBRF | *.pir | Sequences, alignments | NBRF PIR |
| Qual | *.qual | Quality file | Associated with a FASTA file |
| Raw sequence text | *.seq | Sequences | Any file that contains only a sequence |
| Rich Sequence Format | *.rsf | Sequences, alignments | GCGs NetFetch |
| Comma/Tab Separated Values | *.csv, *.tsv | Spreadsheet files | Microsoft Excel |
| SAM/BAM | *.sam, *.bam | Contigs | SAMtools |
| Sequence Chromatograms | *.ab1, *.scf | Raw sequencing trace & sequence | Sequencing machines |
| VCF | *.VCF | Annotations | 1000 Genomes Project |
| Vector NTI sequence | *.gb, *.gp | Nucleotide & protein sequences | Vector NTI |
| Vector NTI/AlignX alignment | *.apr | Alignments | Vector NTI, AlignX |
| Vector NTI Archive | *.ma4, *.pa4, *.oa4, *.ea4, *.ca6 |
Nucleotide & protein sequences, enzyme sets and publications |
Vector NTI |
| Vector NTI/ContigExpress | *.cep | Nucleotide sequence assemblies | Vector NTI |
| Vector NTI database | VNTI Database | Nucleotide & protein sequences, enzyme sets and publications |
Vector NTI |
動作環境
| 対応OS | Windows (10/11 64bit版のみ) macOS 12.7以降 Linux (Ubuntu Desktop LTS 22.04/24.04) |
|---|---|
| CPU | x86 64-bit |
| メモリ | 2048 MB RAM 以上 (最小構成) |
| HDDの空容量 | 2 GB 以上 (最小構成) |
| モニタ | 1024×768以上 (最小構成) |
上記はOS以外は最小構成です。NGS関連の機能を使用する場合はデータ量に依存します。
チュートリアル
アプリケーションごとにチュートリアルが用意されています。
https://www.geneious.com/tutorials(英語)
配列情報マルチ解析ソフトウェア「Geneious」の
カタログを請求する
無料



